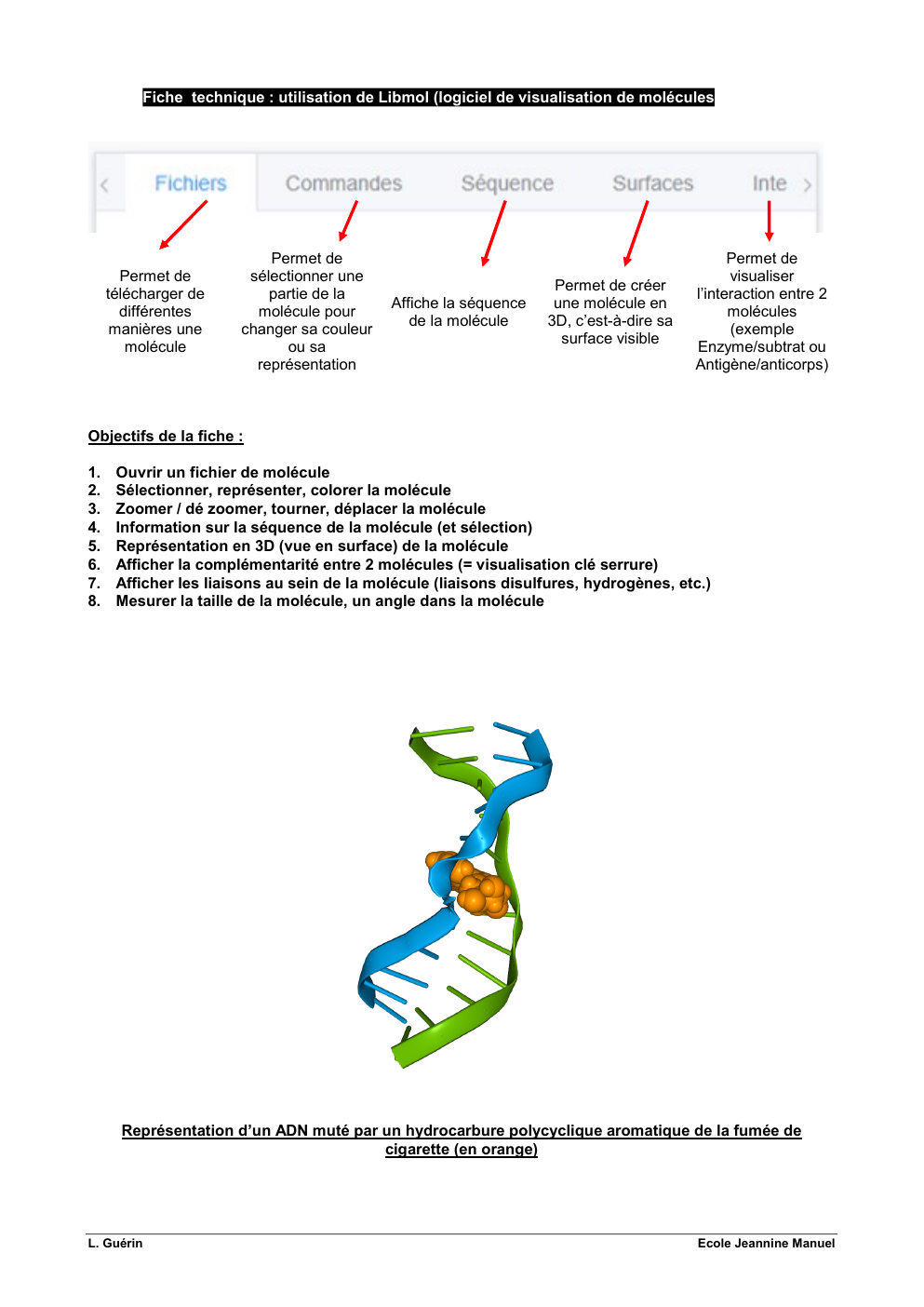
Fiche technique : utilisation de Libmol (logiciel de visualisation de molécules
Publié le 16/03/2026
Extrait du document
«
Fiche technique : utilisation de Libmol (logiciel de visualisation de molécules
Permet de
télécharger de
différentes
manières une
molécule
Permet de
sélectionner une
partie de la
molécule pour
changer sa couleur
ou sa
représentation
Affiche la séquence
de la molécule
Permet de créer
une molécule en
3D, c’est-à-dire sa
surface visible
Permet de
visualiser
l’interaction entre 2
molécules
(exemple
Enzyme/subtrat ou
Antigène/anticorps)
Objectifs de la fiche :
1.
2.
3.
4.
5.
6.
7.
8.
Ouvrir un fichier de molécule
Sélectionner, représenter, colorer la molécule
Zoomer / dé zoomer, tourner, déplacer la molécule
Information sur la séquence de la molécule (et sélection)
Représentation en 3D (vue en surface) de la molécule
Afficher la complémentarité entre 2 molécules (= visualisation clé serrure)
Afficher les liaisons au sein de la molécule (liaisons disulfures, hydrogènes, etc.)
Mesurer la taille de la molécule, un angle dans la molécule
Représentation d’un ADN muté par un hydrocarbure polycyclique aromatique de la fumée de
cigarette (en orange)
L.
Guérin
Ecole Jeannine Manuel
Objectif 1 - Ouvrir un fichier de molécule
Dans le menu « fichier », 3 méthodes pour
télécharger votre molécule en ligne :
Taper son nom dans la librairie de molécule
Taper son code dans la base de PDB
Placer le fichier avec une extension .pdb
dans cet espace
Dans les 3 cas, la fenêtre s’ouvre avec la
molécule affichée selon un mode classique.
Dans
cette
représentation
en
« boules et bâtonnets », les atomes
sont reliés par des liaisons de
covalence.
Le code couleur est indiqué sous la
molécule, ici :
Gris
= carbone
Violet = azote
Rouge = oxygène
Jaune = soufre
L.
Guérin
Ecole Jeannine Manuel
Objectif 2 - Sélectionner, représenter, colorer la molécule
Dans le menu « Commandes », vous pouvez
sélectionner la partie de la molécule qui vous
intéresse.
Méthode 1 - en tapant le nom du nucléotide
(ex : guanine) ou de l’acide aminé (ex :
tyrosine).
Attention à bien valider votre
sélection
Méthode 2 – en choisissant une des options
proposés, mais le choix est restreint ;(
Dans le menu « Commandes », vous pouvez
changer le mode de représentation.
L’option ‘boules et bâtonnets’ est adaptée pour
les petites molécules.
L’option ‘Rubans’ est adaptée pour les grosses
molécules (ADN, protéine) car il simplifie
énormément la vue.
Dans le menu « Commandes », vous pouvez
changer la couleur de la représentation.
L’option « Chaines » permet de distinguer
facilement plusieurs chaines.
L’option « Atomes » permet d’afficher les
atomes suivant le code classique des
chimistes.
L’option « Palette » permet de choisir ses
propres couleurs.
L.
Guérin
Représentation en rubans et en
chaines de la molécule d’insuline
(protéine à 2 chaines)
Ecole Jeannine Manuel
Objectif 3 - Zoomer / dé zoomer, tourner, déplacer la molécule
Actions visées :
Zoomer
Dézoomer
Faire tourner la molécule
Déplacer la molécule
Opérations à effectuer :
Maintenir la touche « shift » maintenue, en même temps
maintenir le clic gauche de la souris et monter la souris.
Maintenir la touche « shift » maintenue, en même temps
maintenir le clic gauche de la souris et descendre la souris.
Maintenir le clic gauche de la souris et en même temps bouger
la souris selon le sens désiré.
Maintenir le clic droit de la souris et en même temps bouger la
souris selon le sens désiré.
Objectif 4 – Information sur la séquence de la molécule (et sélection)
Dans....
»
↓↓↓ APERÇU DU DOCUMENT ↓↓↓
Liens utiles
- TECHNIQUE ET CIVILISATION (fiche bac)
- SCIENCE ET TECHNIQUE (fiche bac)
- CARACTÈRES DE LA TECHNIQUE (fiche bac)
- Fiche de lecture, Arthur Rimbaud, Cahiers de Douai.
- fiche question examinateur: Pourquoi ce recueil s'appelle-t-il Les Cahiers de Douai ?